新闻网讯(通讯员高妍)近日,国际综合性期刊《自然·通讯》(Nature Communications)发表了武汉大学高等研究院教授陈素明团队在异构体水平精准质谱分析领域的最新研究成果。论文题为:“XL-MSDigger: a deep learning-based, versatile solution for cross-linking mass spectrometry”(《XL-MSDigger:基于深度学习的交联质谱分析多功能解决方案》)。武汉大学高等研究院博士生陈默然、郝艳红为论文共同第一作者,陈素明为唯一通讯作者,高等研究院为论文第一署名单位和唯一通讯作者单位。
同分异构体赋予了生命和化学系统的分子结构多样性,这些异构体尽管结构差别微小,却会带来功能的巨大差异。实现异构体水平的精准分析,是深入理解分子结构与功能关系的基石。对于化学修饰肽段,其结构鉴定需要确定氨基酸序列异构与修饰位点异构。传统仅依赖二级碎片离子的鉴定方法,修饰基团位点信息易丢失,假阳性率高,还会因控制错误发现率的要求而限制鉴定深度。此前,该团队率先将基于自注意力机制的深度学习引入多肽多维信息预测,建立了Transformer架构的Deep4D模型。该模型首次实现了磷酸化肽等多修饰类型的碰撞横截面积(CCS)、保留时间、碎片强度联合预测,预测CCS中位数相对误差仅0.72%,显著降低了修饰位点异构鉴定的假阳性率(Anal. Chem. 2023, 95, 7495-7502)。
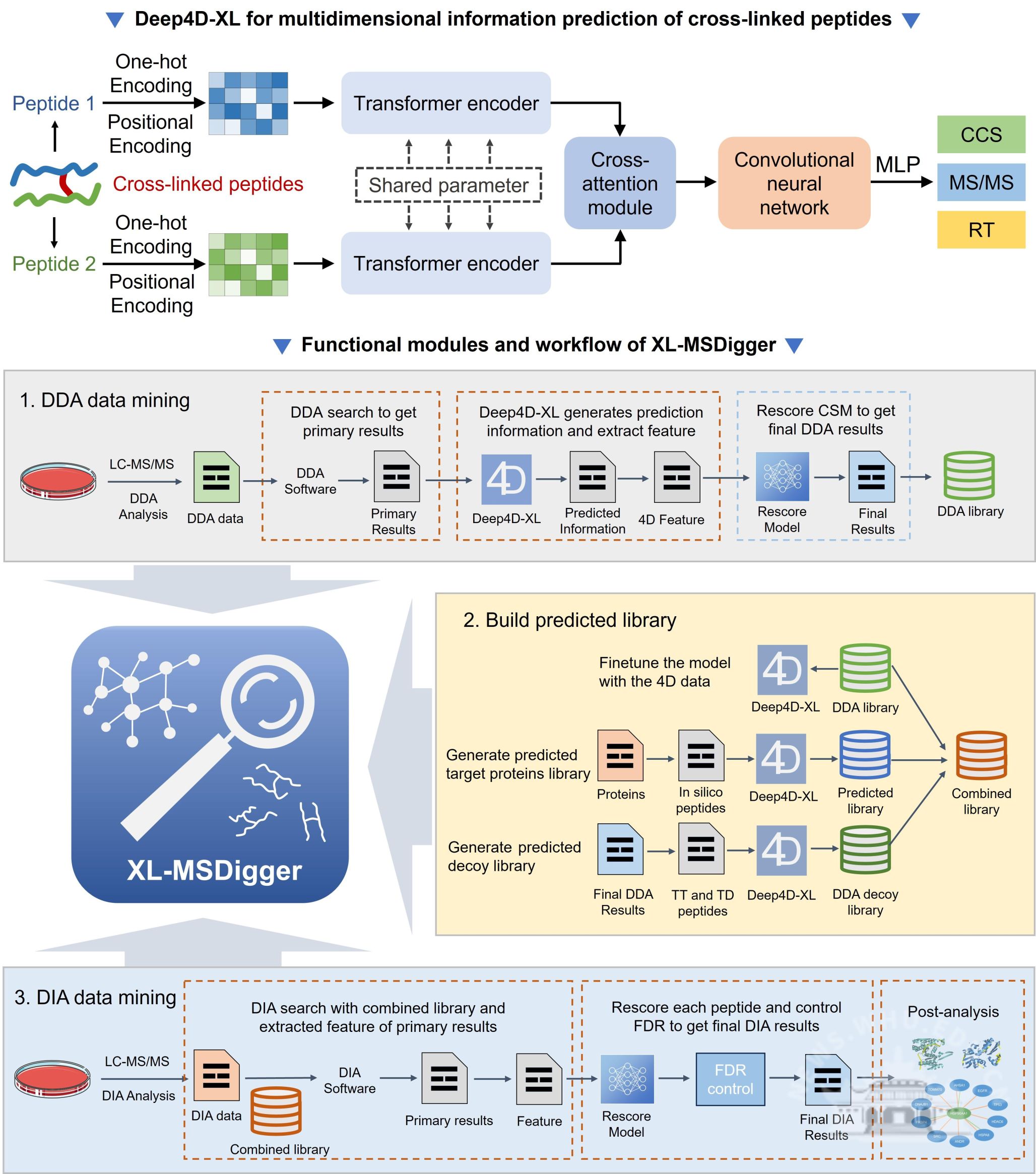
针对结构更为复杂的化学交联肽(同时含两条肽段信息、连接位点不固定、异构形式多样),该团队进一步开发了Deep4D-XL深度学习模型(Nat. Commun.2026, 17, 2554)。该模型创新性地引入孪生网络结构分别表征交联肽的两条肽段,再通过交叉注意力模块融合特征,最后经解码模块输出多维预测。该模型在保留时间预测上与实验值相关性达到R²= 0.97,CCS预测中位相对误差为1.52%,碎片离子强度预测中位点积达0.88。以Deep4D-XL为核心,该团队开发了支持数据依赖采集(DDA)和数据非依赖采集(DIA)模式的交联质谱智能分析平台XL-MSDigger。在DDA分析中,利用多维预测信息提取16个特征,通过深度神经网络重打分,使蛋白质间交联肽谱图匹配数提升107%,蛋白质-蛋白质相互作用鉴定数增加76.3%。在DIA分析中,首次建立了交联肽错误发现率系统评估框架,通过重打分使鉴定数提升约5倍,并实现了基于预测谱库的DIA交联肽分析,鉴定出90条DDA分析未检出的蛋白质内交联肽和多个高置信度蛋白质-蛋白质相互作用。Deep4D-XL是首个公开发表的交联肽多维信息深度学习预测模型。通过高精度多维信息预测实现了此前方法无法实现的交联肽鉴定多维信息重打分,以及诱饵库生成和错误发现率控制环节,在异构体水平显著提升了交联肽结构鉴定的可信度。
该研究得到了国家科技重大专项、国家自然科学基金、国家重点研发计划等项目经费的支持。
论文链接:https://www.nature.com/articles/s41467-026-69489-8